Forschungsinteressen Prof. Dr. Claus Schwechheimer
Regulation des Pflanzenwachstums durch Hormonsignalwege, Proteinphosphorylierung und gerichteten Proteinabbau
Wachstum, Differenzierung und Organbildung müssen während des Wachstums präzise zeitlich und räumlich koordiniert werden, damit robuste Entwicklungsprogramme und flexible Anpassungsreaktionen an Umweltbedingungen möglich sind. Diese Prozesse beruhen in hohem Maße auf der kontrollierten Wahrnehmung, Weiterleitung und Integration von Signalen. Eine zentrale Rolle spielen dabei pflanzliche Hormone wie Auxin und Gibberelline, deren lokale Verteilung und zelluläre Signaltransduktion Wachstumsvorgänge steuern. Ebenso wichtig sind posttranslationale Regulationsmechanismen, insbesondere Proteinphosphorylierung und gerichteter Proteinabbau über das Ubiquitin-Proteasom-System. Diese Mechanismen erlauben es Pflanzen, Entwicklungsentscheidungen schnell, spezifisch und reversibel umzusetzen.
Ein zentraler Schwerpunkt meiner Forschung ist es, zu verstehen, wie pflanzliche Hormonsignalwege auf molekularer Ebene reguliert werden und wie sie Zell- und Gewebewachstum kontrollieren. Insbesondere untersuche ich, wie die Aktivität und subzelluläre Lokalisation von Proteinkinasen den polaren Auxintransport steuern, wie der Gibberellin-Signalweg über DELLA-Proteine die Genexpression und Wachstumsantworten reguliert und wie beide Prozesse mit posttranslationalen Modifikationen und selektivem Proteinabbau verknüpft sind. Dabei interessiert uns besonders, wie Phosphorylierung, Membranpolarisierung und Proteinstabilität zusammenwirken, um gerichtetes Wachstum, Tropismen und Organentwicklung zu ermöglichen.
Darüber hinaus untersucht meine Arbeitsgruppe, wie Signalnetzwerke durch systembiologische Ansätze erfasst und funktionell analysiert werden können. Hierbei kombinieren wir genomische, proteomische und phosphoproteomische Datensätze mit genetischen, biochemischen und zellbiologischen Experimenten, um regulatorische Module zu identifizieren und mechanistisch zu testen. Unser Ziel ist es, allgemeine Prinzipien zu verstehen, mit denen Pflanzen Hormonsignale, Umweltreize und intrazelluläre Regulationsmechanismen integrieren, um Wachstum und Entwicklung präzise zu steuern. Arabidopsis thaliana dient uns dabei als zentrales Modellsystem.
Bisherige Ergebnisse
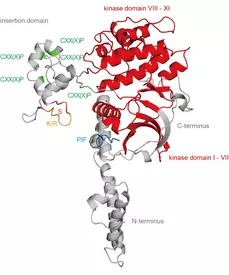
• Wir konnten zeigen, dass die polär lokalisierte AGC-Kinase D6 PROTEIN KINASE (D6PK) ein zentraler Regulator des effizienten Auxintransports ist. D6PK aktiviert PIN-abhängige Auxintransportprozesse und ist damit wesentlich für gerichtetes Wachstum, Organbildung und Tropismen (Zourelidou et al., 2009; Graf et al., 2024).
• Wir konnten zeigen, dass die Plasmamembran-Polarisierung von D6PK durch spezifische Proteinmotive und PDK1-abhängige Phosphorylierung kontrolliert wird. Diese Ergebnisse liefern wichtige mechanistische Einblicke darin, wie die subzelluläre Verteilung von Signalkomponenten die räumliche Präzision des Auxintransports bestimmt (Graf et al., 2024).
• Wir konnten zeigen, dass der Gibberellin-Signalweg über DELLA-Proteine zentrale Wachstums- und Stressreaktionen reguliert. Dabei interagieren DELLA-Proteine mit Wachstumsregulatoren und koppeln hormonelle Signale an Transkriptionskontrolle, etwa unter Kältestress (Lantzouni et al., 2020).
• Wir konnten zeigen, dass der Transport von Gibberellinen selbst aktiv reguliert wird: Das Arabidopsis-Protein NPF3fungiert als Gibberellin-Transporter und stellt damit eine wichtige zusätzliche Ebene der Kontrolle hormoneller Signalverteilung dar (Tal et al., 2016). Zudem konnte gezeigt werden, dass mobile Gibberelline direkt das sekundäre Wachstum und die Xylemexpansion fördern (Ragni et al., 2011).
• Unsere umfangreichen Arbeiten zu B-GATA-Transkriptionsfaktoren, welche wir erstmals als Gibberellin-regulierte Gene identifizierten, zeigen, dass diese wichtige Funktionen bei der Steuerung der Chlorophyllbiosynthese, Chloroplastenentwicklung und Nährstoffantworten übernehmen und damit hormonelle und metabolische Signale mit Entwicklungsprogrammen verknüpfen (Bastakis et al., 2018; Zappone et al., 2026).
• Unsere Arbeiten haben außerdem wesentlich zum Verständnis beigetragen, wie gerichteter Proteinabbau über Cullin-RING-E3-Ubiquitin-Ligasen, das COP9-Signalosom und den NEDD8-Zyklus pflanzliche Entwicklungsprozesse reguliert. Diese Systeme stellen zentrale Schaltstellen dar, um Signalkomponenten kontrolliert zu aktivieren oder abzubauen (Schwechheimer & Calderón Villalobos, 2004; Schwechheimer & Isono, 2010; Mergner et al., 2017).
Forschungsziele
• Wir möchten verstehen, wie die räumliche Organisation von Signalproteinen an der Plasmamembran die Richtung und Effizienz des Auxintransports bestimmt und damit Entwicklungsprozesse auf Organ- und Gewebeebene steuert.
• Wir planen, die molekularen Mechanismen der phosphorylierungsabhängigen Regulation von Kinasen, Transportproteinen und Signalmodulen zu identifizieren, die für polares Wachstum, Tropismen und Morphogenese erforderlich sind.
• Darüber hinaus möchten wir bestimmen, wie Gibberellin-Signalgebung, DELLA-vermittelte Transkriptionskontrolle und Hormontransport zusammenwirken, um Wachstum und Umweltantworten zu koordinieren.
• Ein weiteres Ziel ist es, die Rolle von gerichtetem Proteinabbau und Ubiquitin-/NEDD8-abhängigen Regulationsprozessen bei der Feinabstimmung hormoneller Signalwege aufzuklären.
• Langfristig soll diese Arbeit integrierte Modelle liefern, die beschreiben, wie Pflanzen Hormonsignale, posttranslationale Modifikationen und systemische Regulationsnetzwerke kombinieren, um robuste und zugleich anpassungsfähige Entwicklungsprogramme zu realisieren.
Methoden
Konfokales Live-Cell-Imaging mit fluoreszierenden Reportern zur Analyse von Proteinlokalisation, Membranpolarisierung und Wachstum
Genetische Analysen in Arabidopsis thaliana, einschließlich Mutanten- und Transgenlinien
Biochemische und zellbiologische Charakterisierung von Kinasen, Transportern und Signalproteinen
Proteomik und Phosphoproteomik zur Identifizierung regulatorischer Netzwerke und posttranslationaler Modifikationen
Systembiologische Auswertung genomischer und proteomischer Datensätze zur Generierung und Prüfung funktioneller Hypothesen